Доброго времени суток, господа!
Построена углеродная нанотрубка, и необходимо приблизить к ее поверхности аминную функциональную группу. При расчете энергии во время приближения аминогруппы лицезрю ошибку 2070, а именно ошибку при конвергенции. Отсюда вопрос: возможно ли как-то программно дать директиву, чтобы аминогруппа оптимизировалась при расчете минимальной энергии адсорбции, однако сама нанотрубка при этом не затрагивалась?
Оптимизация в Gaussian
Re: Оптимизация в Gaussian
Чтобы участники форума могли понять, про что Вы пишете и в чем Ваша проблема, неплохо было бы приложить лог расчета или хотя бы скопипастить его конец с тектом ошибки и последними операциями.
Make quantum chemistry, not war
Re: Оптимизация в Gaussian
Код: Выделить всё
Entering Link 1 = C:\G09W\l1.exe PID= 5900.
Copyright © 1988,1990,1992,1993,1995,1998,2003,2009,2013,
Gaussian, Inc. All Rights Reserved.
This is part of the Gaussian(R) 09 program. It is based on
the Gaussian(R) 03 system (copyright 2003, Gaussian, Inc.),
the Gaussian(R) 98 system (copyright 1998, Gaussian, Inc.),
the Gaussian(R) 94 system (copyright 1995, Gaussian, Inc.),
the Gaussian 92(TM) system (copyright 1992, Gaussian, Inc.),
the Gaussian 90(TM) system (copyright 1990, Gaussian, Inc.),
the Gaussian 88(TM) system (copyright 1988, Gaussian, Inc.),
the Gaussian 86(TM) system (copyright 1986, Carnegie Mellon
University), and the Gaussian 82(TM) system (copyright 1983,
Carnegie Mellon University). Gaussian is a federally registered
trademark of Gaussian, Inc.
This software contains proprietary and confidential information,
including trade secrets, belonging to Gaussian, Inc.
This software is provided under written license and may be
used, copied, transmitted, or stored only in accord with that
written license.
The following legend is applicable only to US Government
contracts under FAR:
RESTRICTED RIGHTS LEGEND
Use, reproduction and disclosure by the US Government is
subject to restrictions as set forth in subparagraphs (a)
and © of the Commercial Computer Software - Restricted
Rights clause in FAR 52.227-19.
Gaussian, Inc.
340 Quinnipiac St., Bldg. 40, Wallingford CT 06492
---------------------------------------------------------------
Warning -- This program may not be used in any manner that
competes with the business of Gaussian, Inc. or will provide
assistance to any competitor of Gaussian, Inc. The licensee
of this program is prohibited from giving any competitor of
Gaussian, Inc. access to this program. By using this program,
the user acknowledges that Gaussian, Inc. is engaged in the
business of creating and licensing software in the field of
computational chemistry and represents and warrants to the
licensee that it is not a competitor of Gaussian, Inc. and that
it will not use this program in any manner prohibited above.
---------------------------------------------------------------
Cite this work as:
Gaussian 09, Revision D.01,
M. J. Frisch, G. W. Trucks, H. B. Schlegel, G. E. Scuseria,
M. A. Robb, J. R. Cheeseman, G. Scalmani, V. Barone, B. Mennucci,
G. A. Petersson, H. Nakatsuji, M. Caricato, X. Li, H. P. Hratchian,
A. F. Izmaylov, J. Bloino, G. Zheng, J. L. Sonnenberg, M. Hada,
M. Ehara, K. Toyota, R. Fukuda, J. Hasegawa, M. Ishida, T. Nakajima,
Y. Honda, O. Kitao, H. Nakai, T. Vreven, J. A. Montgomery, Jr.,
J. E. Peralta, F. Ogliaro, M. Bearpark, J. J. Heyd, E. Brothers,
K. N. Kudin, V. N. Staroverov, T. Keith, R. Kobayashi, J. Normand,
K. Raghavachari, A. Rendell, J. C. Burant, S. S. Iyengar, J. Tomasi,
M. Cossi, N. Rega, J. M. Millam, M. Klene, J. E. Knox, J. B. Cross,
V. Bakken, C. Adamo, J. Jaramillo, R. Gomperts, R. E. Stratmann,
O. Yazyev, A. J. Austin, R. Cammi, C. Pomelli, J. W. Ochterski,
R. L. Martin, K. Morokuma, V. G. Zakrzewski, G. A. Voth,
P. Salvador, J. J. Dannenberg, S. Dapprich, A. D. Daniels,
O. Farkas, J. B. Foresman, J. V. Ortiz, J. Cioslowski,
and D. J. Fox, Gaussian, Inc., Wallingford CT, 2013.
******************************************
Gaussian 09: IA32W-G09RevD.01 24-Apr-2013
11-Feb-2018
******************************************
%mem=1000MB
%nprocshared=4
Will use up to 4 processors via shared memory.
%chk=C:\G09W\Scratch\dryuchkov\AMINOGROUP\TUBE_AMIN_ENERGY_16.chk
-------------------------------
# b3lyp/3-21g geom=connectivity
-------------------------------
1/38=1,57=2/1;
2/12=2,17=6,18=5,40=1/2;
3/5=5,11=2,16=1,25=1,30=1,74=-5/1,2,3;
4//1;
5/5=2,38=5/2;
6/7=2,8=2,9=2,10=2,28=1/1;
99/5=1,9=1/99;
-------------------
Title Card Required
-------------------
Symbolic Z-matrix:
Charge = 0 Multiplicity = 2
C
C 1 B1
C 2 B2 1 A1
C 1 B3 2 A2 3 D1 0
C 3 B4 2 A3 1 D2 0
C 4 B5 1 A4 2 D3 0
C 5 B6 3 A5 2 D4 0
C 7 B7 5 A6 3 D5 0
C 6 B8 4 A7 1 D6 0
C 9 B9 6 A8 4 D7 0
C 8 B10 7 A9 5 D8 0
C 10 B11 9 A10 6 D9 0
C 11 B12 8 A11 7 D10 0
C 13 B13 11 A12 8 D11 0
C 12 B14 10 A13 9 D12 0
C 15 B15 12 A14 10 D13 0
C 2 B16 1 A15 4 D14 0
C 16 B17 15 A16 12 D15 0
C 3 B18 2 A17 1 D16 0
C 5 B19 3 A18 2 D17 0
C 8 B20 7 A19 5 D18 0
C 11 B21 8 A20 7 D19 0
C 14 B22 13 A21 11 D20 0
C 17 B23 2 A22 1 D21 0
C 19 B24 3 A23 2 D22 0
C 22 B25 11 A24 8 D23 0
C 23 B26 14 A25 13 D24 0
C 19 B27 3 A26 2 D25 0
C 20 B28 5 A27 3 D26 0
C 22 B29 11 A28 8 D27 0
C 28 B30 19 A29 3 D28 0
C 29 B31 20 A30 5 D29 0
C 29 B32 20 A31 5 D30 0
C 30 B33 22 A32 11 D31 0
C 30 B34 22 A33 11 D32 0
C 28 B35 19 A34 3 D33 0
C 31 B36 28 A35 19 D34 0
C 32 B37 29 A36 20 D35 0
C 33 B38 29 A37 20 D36 0
C 34 B39 30 A38 22 D37 0
C 35 B40 30 A39 22 D38 0
C 36 B41 28 A40 19 D39 0
C 37 B42 31 A41 28 D40 0
C 40 B43 34 A42 30 D41 0
C 41 B44 35 A43 30 D42 0
C 37 B45 31 A44 28 D43 0
C 38 B46 32 A45 29 D44 0
C 40 B47 34 A46 30 D45 0
C 46 B48 37 A47 31 D46 0
C 47 B49 38 A48 32 D47 0
C 47 B50 38 A49 32 D48 0
C 48 B51 40 A50 34 D49 0
C 48 B52 40 A51 34 D50 0
C 46 B53 37 A52 31 D51 0
C 49 B54 46 A53 37 D52 0
C 50 B55 47 A54 38 D53 0
C 51 B56 47 A55 38 D54 0
C 52 B57 48 A56 40 D55 0
C 53 B58 48 A57 40 D56 0
C 54 B59 46 A58 37 D57 0
C 55 B60 49 A59 46 D58 0
C 58 B61 52 A60 48 D59 0
C 59 B62 53 A61 48 D60 0
C 55 B63 49 A62 46 D61 0
C 56 B64 50 A63 47 D62 0
C 58 B65 52 A64 48 D63 0
C 64 B66 55 A65 49 D64 0
C 65 B67 56 A66 50 D65 0
C 65 B68 56 A67 50 D66 0
C 66 B69 58 A68 52 D67 0
C 66 B70 58 A69 52 D68 0
C 64 B71 55 A70 49 D69 0
H 9 B72 6 A71 4 D70 0
H 12 B73 10 A72 9 D71 0
H 6 B74 4 A73 1 D72 0
H 1 B75 4 A74 6 D73 0
H 18 B76 16 A75 15 D74 0
H 15 B77 12 A76 10 D75 0
H 68 B78 65 A77 56 D76 0
H 67 B79 64 A78 55 D77 0
H 72 B80 64 A79 55 D78 0
H 71 B81 66 A80 58 D79 0
H 70 B82 66 A81 58 D80 0
H 69 B83 65 A82 56 D81 0
C 12 B84 10 A83 9 D82 0
C 30 B85 22 A84 11 D83 0
C 16 B86 15 A85 12 D84 0
C 27 B87 23 A86 14 D85 0
C 48 B88 40 A87 34 D86 0
C 58 B89 52 A88 48 D87 0
C 67 B90 64 A89 55 D88 0
C 63 B91 59 A90 53 D89 0
C 55 B92 49 A91 46 D90 0
C 70 B93 66 A92 58 D91 0
C 65 B94 56 A93 50 D92 0
C 43 B95 37 A94 31 D93 0
C 44 B96 40 A95 34 D94 0
C 47 B97 38 A96 32 D95 0
C 25 B98 19 A97 3 D96 0
C 46 B99 37 A98 31 D97 0
C 45 B100 41 A99 35 D98 0
C 28 B101 19 A100 3 D99 0
C 3 B102 2 A101 1 D100 0
C 26 B103 22 A102 11 D101 0
C 29 B104 20 A103 5 D102 0
C 11 B105 8 A104 7 D103 0
C 7 B106 5 A105 3 D104 0
C 1 B107 4 A106 6 D105 0
N 34 B108 30 A107 22 D106 0
H 109 B109 34 A108 30 D107 0
H 109 B110 34 A109 30 D108 0
Variables:
B1 2.4681
B2 1.43347
B3 1.41737
B4 2.42357
B5 1.4228
B6 1.45697
B7 1.45707
B8 2.3353
B9 1.42292
B10 2.42362
B11 1.41734
B12 1.43356
B13 1.43528
B14 2.3938
B15 1.43314
B16 1.43558
B17 1.43335
B18 1.42934
B19 1.41413
B20 1.41397
B21 1.42917
B22 1.41423
B23 1.4137
B24 1.43371
B25 1.43372
B26 1.45964
B27 2.4705
B28 2.47325
B29 2.47072
B30 1.43536
B31 1.4616
B32 1.46171
B33 1.43546
B34 1.43916
B35 1.43944
B36 1.42354
B37 1.40869
B38 1.40856
B39 1.42342
B40 1.40873
B41 1.40834
B42 1.43542
B43 1.43551
B44 1.4616
B45 2.47167
B46 2.47344
B47 2.47178
B48 1.43373
B49 1.45973
B50 1.45979
B51 1.43369
B52 1.43921
B53 1.43934
B54 1.42929
B55 1.41407
B56 1.41395
B57 1.42928
B58 1.4141
B59 1.41392
B60 1.43347
B61 1.43352
B62 1.45706
B63 2.48212
B64 2.4776
B65 2.48217
B66 1.41733
B67 1.4332
B68 1.43324
B69 1.41733
B70 1.42284
B71 1.42293
B72 1.08488
B73 1.08561
B74 1.08489
B75 1.08562
B76 1.08486
B77 1.08489
B78 1.08488
B79 1.08561
B80 1.08488
B81 1.08488
B82 1.08562
B83 1.08487
B84 1.4173
B85 1.42453
B86 1.41385
B87 1.39605
B88 1.42454
B89 1.43348
B90 1.41732
B91 1.41395
B92 1.43353
B93 1.41732
B94 1.41393
B95 1.42454
B96 1.42442
B97 1.39619
B98 1.42452
B99 1.42438
B100 1.39618
B101 1.42441
B102 1.43347
B103 1.42444
B104 1.39621
B105 1.43354
B106 1.41404
B107 1.41729
B108 1.6
B109 1.05573
B110 1.05573
A1 89.27346
A2 88.97623
A3 131.80044
A4 114.88092
A5 128.50292
A6 111.12142
A7 125.97166
A8 125.96186
A9 128.48101
A10 114.8583
A11 131.77231
A12 115.3038
A13 133.15742
A14 129.29235
A15 143.8857
A16 109.0854
A17 119.4473
A18 90.22531
A19 119.63939
A20 89.91014
A21 119.72317
A22 119.73179
A23 119.52918
A24 119.5351
A25 119.6997
A26 149.61015
A27 148.97379
A28 149.60967
A29 89.3086
A30 89.11733
A31 142.35246
A32 89.30547
A33 144.76669
A34 144.76714
A35 119.60284
A36 119.90579
A37 119.90628
A38 119.60143
A39 119.85297
A40 119.86068
A41 119.59985
A42 119.60447
A43 119.9072
A44 149.67474
A45 149.21507
A46 149.67564
A47 89.30238
A48 89.15314
A49 142.51103
A50 89.302
A51 144.96272
A52 144.95866
A53 119.53454
A54 119.70023
A55 119.70121
A56 119.53271
A57 119.78277
A58 119.78611
A59 119.44457
A60 119.44648
A61 119.63426
A62 149.89307
A63 149.48257
A64 149.89429
A65 89.08052
A66 89.18394
A67 140.89678
A68 89.0789
A69 143.66701
A70 143.66185
A71 90.39843
A72 119.02249
A73 119.74273
A74 119.02133
A75 119.77621
A76 91.05109
A77 119.76724
A78 119.02227
A79 119.74907
A80 119.7456
A81 119.02256
A82 119.76951
A83 117.55303
A84 30.29495
A85 120.03992
A86 119.98116
A87 30.32668
A88 119.44497
A89 117.55606
A90 119.29542
A91 119.44592
A92 117.55671
A93 30.85656
A94 119.59693
A95 119.59921
A96 30.8299
A97 119.62651
A98 30.32646
A99 119.86316
A100 30.29228
A101 116.01159
A102 119.63144
A103 30.74586
A104 32.38065
A105 119.29389
A106 117.55703
A107 101.71512
A108 131.12028
A109 126.40233
D1 -21.47848
D2 59.05875
D3 -139.50826
D4 1.66532
D5 82.35303
D6 84.20694
D7 0.00161
D8 -82.33479
D9 -84.18098
D10 -1.64999
D11 93.47935
D12 92.37737
D13 -2.21766
D14 113.55685
D15 -81.83074
D16 179.21883
D17 131.08558
D18 34.92986
D19 129.47803
D20 26.64338
D21 -155.24695
D22 -153.20827
D23 13.34416
D24 -148.03878
D25 -0.78722
D26 -134.09834
D27 -139.05814
D28 -179.51383
D29 179.40608
D30 54.1594
D31 179.52181
D32 43.76653
D33 -43.77833
D34 179.83406
D35 179.8443
D36 151.26727
D37 -179.8297
D38 155.9227
D39 -155.9137
D40 -152.87104
D41 152.85391
D42 -148.73288
D43 -0.21743
D44 0.15515
D45 0.20777
D46 -179.71281
D47 -179.72984
D48 54.11466
D49 179.71536
D50 43.07905
D51 -43.10877
D52 179.72482
D53 -179.64833
D54 151.2171
D55 -179.72273
D56 156.31431
D57 -156.2909
D58 -153.19552
D59 153.19192
D60 -149.37606
D61 0.44864
D62 -1.64962
D63 -0.46321
D64 -178.61688
D65 179.02917
D66 58.94049
D67 178.62279
D68 45.12637
D69 -45.15361
D70 -128.16837
D71 -28.25312
D72 -30.89851
D73 28.22972
D74 -37.89509
D75 -133.26341
D76 177.42366
D77 179.95256
D78 -157.82339
D79 157.8316
D80 -179.9528
D81 151.57209
D82 127.99318
D83 -0.37809
D84 62.47255
D85 179.96315
D86 -0.37939
D87 -0.5498
D88 23.70158
D89 179.83747
D90 0.54333
D91 -23.70093
D92 -0.27388
D93 179.77569
D94 -179.77408
D95 -0.27655
D96 179.77695
D97 0.38776
D98 179.84181
D99 0.38467
D100 24.5758
D101 -179.77755
D102 -0.05219
D103 -73.52347
D104 -62.55653
D105 -128.02017
D106 83.22493
D107 -56.49339
D108 117.74501
Stoichiometry C96H14N(2)
Framework group C1[X(C96H14N)]
Deg. of freedom 327
Full point group C1 NOp 1
Largest Abelian subgroup C1 NOp 1
Largest concise Abelian subgroup C1 NOp 1
Standard orientation:
---------------------------------------------------------------------
Center Atomic Atomic Coordinates (Angstroms)
Number Number Type X Y Z
---------------------------------------------------------------------
1 6 0 -7.805926 -0.000109 -2.324720
2 6 0 -5.671202 -1.215823 -2.086958
3 6 0 -4.967924 -0.000070 -2.373627
4 6 0 -7.113798 1.211999 -2.078341
5 6 0 -4.958647 2.158889 -1.272500
6 6 0 -7.802902 2.135919 -1.244151
7 6 0 -5.676299 2.568091 -0.072377
8 6 0 -4.963239 2.159431 1.130779
9 6 0 -7.807528 2.136372 1.091141
10 6 0 -7.121563 1.212602 1.928288
11 6 0 -4.976882 0.000444 2.231927
12 6 0 -7.814760 0.000503 2.171507
13 6 0 -5.679065 -1.215208 1.941688
14 6 0 -4.963396 -2.158289 1.130238
15 6 0 -7.807427 -2.135250 1.090406
16 6 0 -7.090120 -2.559914 -0.075368
17 6 0 -4.958386 -2.159420 -1.273069
18 6 0 -7.802983 -2.136259 -1.244488
19 6 0 -3.538602 -0.000062 -2.380856
20 6 0 -3.544521 2.161130 -1.276570
21 6 0 -3.549304 2.161680 1.140396
22 6 0 -3.547766 0.000423 2.244661
23 6 0 -3.549197 -2.160561 1.139891
24 6 0 -3.544698 -2.161669 -1.277149
25 6 0 -2.830499 1.212013 -2.089344
26 6 0 -2.838384 1.212441 1.955948
27 6 0 -2.818359 -2.535073 -0.066827
28 6 0 -1.406041 -1.213253 -2.091493
29 6 0 -1.422213 2.538795 -0.064075
30 6 0 -1.413953 -1.212821 1.963034
31 6 0 -0.696410 -0.000039 -2.382688
32 6 0 -0.691143 2.154375 -1.269905
33 6 0 -0.695798 2.154776 1.144829
34 6 0 -0.705436 0.000342 2.257635
35 6 0 -0.695968 -2.153939 1.144519
36 6 0 -0.690977 -2.154715 -1.270320
37 6 0 0.727125 -0.000058 -2.379912
38 6 0 0.717545 2.154352 -1.267149
39 6 0 0.712761 2.154691 1.147564
40 6 0 0.717978 0.000328 2.260355
41 6 0 0.712758 -2.153915 1.147255
42 6 0 0.717362 -2.154698 -1.267514
43 6 0 1.435577 1.213177 -2.085676
44 6 0 1.427705 1.213659 1.969131
45 6 0 1.443856 -2.538484 -0.058513
46 6 0 2.860007 -1.212155 -2.078580
47 6 0 2.840108 2.535144 -0.055683
48 6 0 2.852123 -1.211675 1.966818
49 6 0 3.569358 -0.000039 -2.366984
50 6 0 3.570955 2.161172 -1.262672
51 6 0 3.566286 2.161591 1.154323
52 6 0 3.560304 0.000306 2.258454
53 6 0 3.566126 -2.160812 1.154002
54 6 0 3.570977 -2.161373 -1.262975
55 6 0 4.998589 -0.000057 -2.354333
56 6 0 4.984993 2.158946 -1.253093
57 6 0 4.980227 2.159332 1.150259
58 6 0 4.989568 0.000285 2.251306
59 6 0 4.980215 -2.158698 1.150010
60 6 0 4.984866 -2.159167 -1.253369
61 6 0 5.700731 1.215554 -2.064311
62 6 0 5.692894 1.216022 1.964415
63 6 0 5.697902 -2.567905 -0.050197
64 6 0 7.143229 -1.212185 -2.050707
65 6 0 7.111900 2.559990 -0.047296
66 6 0 7.135428 -1.211778 1.955745
67 6 0 7.836405 -0.000122 -2.294070
68 6 0 7.829164 2.135784 -1.213331
69 6 0 7.824642 2.136262 1.121735
70 6 0 7.827608 0.000249 2.202125
71 6 0 7.824513 -2.135714 1.121489
72 6 0 7.829156 -2.136029 -1.213604
73 1 0 -8.892019 2.165001 1.096532
74 1 0 -8.900107 0.000544 2.147600
75 1 0 -8.887374 2.164448 -1.253613
76 1 0 -8.891366 -0.000156 -2.305113
77 1 0 -8.887405 -2.165475 -1.254376
78 1 0 -8.891923 -2.163996 1.095772
79 1 0 8.913653 2.164570 -1.218731
80 1 0 8.921753 -0.000162 -2.270214
81 1 0 8.913632 -2.164920 -1.219068
82 1 0 8.908970 -2.164510 1.131108
83 1 0 8.913048 0.000255 2.182519
84 1 0 8.909089 2.165123 1.131416
85 6 0 -7.121644 -1.211451 1.927570
86 6 0 -2.838464 -1.211626 1.955518
87 6 0 -5.676295 -2.568193 -0.072525
88 6 0 -1.422313 -2.538592 -0.064081
89 6 0 1.427588 -1.212839 1.968710
90 6 0 5.692803 -1.215367 1.964050
91 6 0 7.143316 1.211906 -2.050329
92 6 0 7.111828 -2.559774 -0.047413
93 6 0 5.700761 -1.215822 -2.064735
94 6 0 7.135442 1.212330 1.955998
95 6 0 5.697993 2.568186 -0.050070
96 6 0 2.860096 1.211955 -2.078200
97 6 0 2.852126 1.212377 1.967135
98 6 0 1.443923 2.538789 -0.058415
99 6 0 -1.405981 1.213236 -2.091291
100 6 0 1.435644 -1.213311 -2.086081
101 6 0 2.840033 -2.534949 -0.055796
102 6 0 -2.830452 -1.212051 -2.089557
103 6 0 -5.671179 1.215630 -2.086696
104 6 0 -1.413966 1.213615 1.963401
105 6 0 -2.818417 2.535198 -0.066779
106 6 0 -5.679098 1.216201 1.942310
107 6 0 -7.090309 2.559813 -0.075160
108 6 0 -7.113728 -1.212117 -2.078551
109 7 0 -0.712739 0.000475 3.857618
110 1 0 -1.509994 -0.043491 4.548282
111 1 0 0.133250 -0.037849 4.488013
---------------------------------------------------------------------
Rotational constants (GHZ): 0.0717816 0.0157709 0.0156622
Standard basis: 3-21G (6D, 7F)
There are 901 symmetry adapted cartesian basis functions of A symmetry.
There are 901 symmetry adapted basis functions of A symmetry.
901 basis functions, 1497 primitive gaussians, 901 cartesian basis functions
299 alpha electrons 298 beta electrons
nuclear repulsion energy 17694.8832514402 Hartrees.
NAtoms= 111 NActive= 111 NUniq= 111 SFac= 1.00D+00 NAtFMM= 60 NAOKFM=T Big=T
Integral buffers will be 262144 words long.
Raffenetti 2 integral format.
Two-electron integral symmetry is turned on.
One-electron integrals computed using PRISM.
NBasis= 901 RedAO= T EigKep= 6.01D-04 NBF= 901
NBsUse= 901 1.00D-06 EigRej= -1.00D+00 NBFU= 901
ExpMin= 1.83D-01 ExpMax= 2.43D+02 ExpMxC= 2.43D+02 IAcc=1 IRadAn= 1 AccDes= 0.00D+00
Harris functional with IExCor= 402 and IRadAn= 1 diagonalized for initial guess.
HarFok: IExCor= 402 AccDes= 0.00D+00 IRadAn= 1 IDoV= 1 UseB2=F ITyADJ=14
ICtDFT= 3500011 ScaDFX= 1.000000 1.000000 1.000000 1.000000
FoFCou: FMM=F IPFlag= 0 FMFlag= 100000 FMFlg1= 2001
NFxFlg= 0 DoJE=T BraDBF=F KetDBF=T FulRan=T
wScrn= 0.000000 ICntrl= 500 IOpCl= 0 I1Cent= 200000004 NGrid= 0
NMat0= 1 NMatS0= 1 NMatT0= 0 NMatD0= 1 NMtDS0= 0 NMtDT0= 0
Petite list used in FoFCou.
Initial guess <Sx>= 0.0000 <Sy>= 0.0000 <Sz>= 0.5000 <S**2>= 0.7500 S= 0.5000
Requested convergence on RMS density matrix=1.00D-08 within 128 cycles.
Requested convergence on MAX density matrix=1.00D-06.
Requested convergence on energy=1.00D-06.
No special actions if energy rises.
Integral accuracy reduced to 1.0D-05 until final iterations.
EnCoef did 6 forward-backward iterations
EnCoef did 1 forward-backward iterations
EnCoef did 2 forward-backward iterations
EnCoef did 5 forward-backward iterations
Initial convergence to 1.0D-05 achieved. Increase integral accuracy.
Rare condition: small coef for last iteration: 0.000D+00
Rare condition: small coef for last iteration: 0.000D+00
Rare condition: small coef for last iteration: 0.000D+00
Rare condition: small coef for last iteration: 0.000D+00
Restarting incremental Fock formation.
Restarting incremental Fock formation.
Restarting incremental Fock formation.
Restarting incremental Fock formation.
Restarting incremental Fock formation.
>>>>>>>>>> Convergence criterion not met.
SCF Done: E(UB3LYP) = -3700.12080058 A.U. after 129 cycles
NFock=128 Conv=0.54D-06 -V/T= 2.0078
<Sx>= 0.0000 <Sy>= 0.0000 <Sz>= 0.5000 <S**2>= 0.8919 S= 0.5686
<L.S>= 0.000000000000E+00
Annihilation of the first spin contaminant:
S**2 before annihilation 0.8919, after 0.7687
Convergence failure -- run terminated.
Error termination via Lnk1e in C:\G09W\l502.exe at Sun Feb 11 04:55:43 2018.
Job cpu time: 0 days 4 hours 47 minutes 50.0 seconds.
File lengths (MBytes): RWF= 766 Int= 0 D2E= 0 Chk= 19 Scr= 1
Re: Оптимизация в Gaussian
Задайте систему в декартовых координатах и добавьте столбец сразу после символа элемента -1 для всех углеродных атомов и 0 для азота и водородов. Только замораживание атомов не поможет поскольку ошибка не в сходимости оптимизации, а в сходимости SCF. Можно попробовать предоптимизировать в полуэмпирике (геометрия явно неоптимальна), поиграть с SCF=XQC  SCF=Fermi
SCF=Fermi 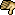
Впрочем мне видится мало смысла в подобном расчете
1) ввиду крайней малости базиса и отсутствия дисперсионной поправки которая принципиальная как минимум для физисорбции). Если принципиально удешевить расчет - экономьте на функционале, скажем PBEPBE
2) если речь о физисорбции (я не уверен что она реализуется для столь малых трубок) то возникает вопрос точно ли хотят считать радикал а не какой то амин.
3) если речь о хемисорбции (стартовая геометрия на это намекает) то нельзя замораживать оптимизацию как минимум атома к которому идет присоединение (а по уму - и еще штук 3-9 ближайших).
Впрочем мне видится мало смысла в подобном расчете
1) ввиду крайней малости базиса и отсутствия дисперсионной поправки которая принципиальная как минимум для физисорбции). Если принципиально удешевить расчет - экономьте на функционале, скажем PBEPBE
2) если речь о физисорбции (я не уверен что она реализуется для столь малых трубок) то возникает вопрос точно ли хотят считать радикал а не какой то амин.
3) если речь о хемисорбции (стартовая геометрия на это намекает) то нельзя замораживать оптимизацию как минимум атома к которому идет присоединение (а по уму - и еще штук 3-9 ближайших).
Кто сейчас на конференции
Сейчас этот форум просматривают: нет зарегистрированных пользователей и 22 гостя